La frustración de las proteínas
Las conocemos como ingredientes saludables de nuestra dieta. Pero puede ser difícil imaginarlas como moléculas con insatisfacciones permanentes. Analizar su “malestar” no es tarea de psicólogos. Es una empresa llevada a cabo por científicos de áreas diversas que quieren comprender cómo hacen las proteínas para efectuar la multimillonaria cantidad de acciones que sostienen la vida.
Descargar archivo MP3 de Diego Ferreiro
Habitan todos los recovecos de la materia viva adoptando formas extravagantes, casi monstruosas. Su apariencia grotesca contrasta con la buena imagen que de ellas se transmite. Pero es precisamente su capacidad de adoptar estructuras increíblemente variadas la que otorga a estos diminutos esperpentos su estatus de “pilares de la vida”. Porque las proteínas –de ellas estamos hablando– son moléculas que pueden asumir conformaciones muy diversas y, por ello, desempeñar numerosas funciones que son vitales para los seres vivos.
Algunas forman parte de la estructura básica de todos los tejidos vegetales y animales. Es decir, constituyen una parte importante del “armazón” que le da soporte a las células que constituyen órganos como la piel, las hojas, el hígado, las raíces o el cerebro.
Otras actúan como “máquinas” microscópicas que ejecutan tareas específicas. Por ejemplo, la hemoglobina es la proteína que transporta el oxígeno por la sangre; las inmunoglobulinas son los anticuerpos que nos defienden de las infecciones; la actina y la miosina son responsables de la contracción muscular; la trombina y el fibrinógeno contribuyen en la formación del coágulo sanguíneo, y la insulina y el glucagón regulan los niveles de glucosa en la sangre.
Hay proteínas que ejecutan un programa de autodestrucción que conduce a la muerte celular y hay otras que trabajan para que una célula se multiplique.
Hay proteínas que nos ayudan a digerir los alimentos y hay otras que pueden matarnos, como las toxinas producidas por algunas bacterias o las que componen el veneno de ciertas serpientes.
Hay proteínas que se encargan de destruir compuestos químicos y hay otras que se dedican a construir grandes moléculas como, por ejemplo, el ADN. Incluso, hay proteínas que se dedican a fabricar proteínas.
Como se ve, hay proteínas “para todos los gustos”.
De hecho, el organismo de un solo ser humano tiene decenas de miles de proteínas diferentes que realizan decenas de miles de funciones diferentes.
Este número no incluye –obviamente– a la proteína que forma la tela de araña o a la que constituye el capullo del gusano de seda. Ni tampoco a la albúmina que conforma la clara del huevo o a la plastocianina, que posibilita la fotosíntesis en las plantas.
Si se listaran todas las proteínas distintas –conocidas hasta el momento– que existen en la naturaleza su número sería multimillonario.
En otras palabras, lo que conocemos con el nombre genérico de “proteínas” es un gigantesco conjunto de moléculas diferentes, cada una de las cuales ejecuta una acción particular.
Posibilidades infinitas
No es lo mismo una esponja que un japonés. Sin embargo, ambas palabras están formadas por exactamente las mismas letras. Son anagramas. Lo mismo que argentino e ignorante, o animales y milanesa.
De igual modo, podría decirse que las proteínas están formadas por un número limitado de “letras” que pueden combinarse para crear “palabras” diferentes.
En esta analogía, esas “letras” son los aminoácidos, un conjunto de moléculas relativamente pequeñas que se unen entre sí para construir moléculas mucho más grandes (macromoléculas) que son, precisamente, las proteínas.
Como el alfabeto proteico está formado por veinte letras –es decir, hay veinte aminoácidos distintos– la cantidad de anagramas que podrían formarse es inmensa.
Pero no todas las proteínas utilizan los 20 aminoácidos para conformar su estructura. Algunas poseen apenas unas pocas letras distintas. No obstante, las repiten.
Mediante el uso redundante de aminoácidos, las proteínas pueden alcanzar longitudes muy diversas, que van desde unas pocas decenas de aminoácidos hasta varios miles. De hecho, la proteína más larga que se conoce, la conectina, que cumple un papel fundamental en la contracción muscular, está compuesta por 34.350 aminoácidos.
En definitiva, hablamos de un alfabeto de veinte letras que pueden mezclarse y repetirse de tantas maneras como sea posible para dar como resultado un diccionario infinito. Un glosario ilimitado que permite explicar la multimillonaria diversidad de moléculas proteicas que hacen posible la también multimillonaria variedad de acciones que sustentan la vida.
Origami molecular
La incalculable heterogeneidad de las proteínas no debería sorprender a nadie. En el colegio, o a través de las crónicas y series policiales, hemos aprendido que otra macromolécula, el ADN, también es interminablemente distinto y que, por eso, permite identificar a cada una de las miles de millones de personas que habitan nuestro mundo. Sabemos que la infinidad de seres vivos que pueblan el planeta tienen genomas diferentes. Que entre mamá, papá, cada árbol de la vereda, cada uno de los gatos del vecino y nosotros mismos, existen diferencias genéticas. Y el ADN hace posible toda esa diversidad con un “simple alfabeto” de tan solo cuatro “letras”.
Pero las proteínas tienen una propiedad distintiva: pueden adquirir formas increíblemente variadas.
Como en el origami, el arte japonés que crea figuras de formas diversas tan solo doblando papel, las proteínas adquieren sus innumerables formatos “doblando” la cadena de aminoácidos que las constituyen.
Porque ni bien es fabricada en la célula –mediante la unión sucesiva de un aminoácido con otro– esa cadena lineal de “letras” empieza a doblarse y enrollarse sobre sí misma, un proceso denominado “plegado”.
Así, dependiendo de los aminoácidos que la compongan, la proteína se plegará y adoptará una estructura tridimensional particular y propia que determinará su localización y su función.
¿Por qué se pliega una proteína? Porque desde el mismo momento de su nacimiento interacciona con los componentes de su entorno, los cuales ejercen sobre ella un sinnúmero de fuerzas.
Por ejemplo, el agua que está presente a su alrededor tiene un papel fundamental en el plegado. Porque la macromolécula posee regiones que, como el aceite, rechazan el agua y buscan “esconderse” de ella. Para ocultar esas zonas hidrofóbicas, la proteína se pliega sobre sí misma y crea “bolsillos” donde guarecerlas. Al mismo tiempo, deja expuestas hacia el agua sus partes hidrofílicas, es decir, aquellas que “se llevan bien” con el agua.
Este plegado modifica la disposición de los aminoácidos en el espacio. Aquellos que originalmente estaban alejados entre sí pueden quedar muy cerca. Esta proximidad favorece la interacción entre ellos y, en consecuencia, la posibilidad de que establezcan uniones que, aunque son débiles, en conjunto suman la fuerza necesaria para plegar aun más la macromolécula.
Así pues, no existe una fuerza única responsable del plegado de la proteína, sino que dicho fenómeno depende de un conjunto de interacciones, muchas de ellas de escasa intensidad.
Aun más, en algunos casos, dos o más de estas cadenas tridimensionales plegadas pueden unirse entre sí para conformar proteínas más complejas.
Tendencia pachorra
Todo el proceso de plegado de una proteína puede ocurrir en menos de un segundo. Un tiempo que, en términos vitales, parece insignificante. Sin embargo, la gran mayoría de las reacciones químicas que ocurren en los organismos vivos suceden en lapsos menores a un segundo.
Podría pensarse entonces en las moléculas como un conjunto de entes sumamente ávidos por hacer su trabajo.
Pero, en realidad, todo lo que hacen estas partículas tiene una única finalidad: alcanzar un estado de reposo. Ese momento, si se alcanzara, sería aquel en el que las moléculas dejarían de moverse.
No es difícil imaginar que, si eso ocurriera, la vida –al menos tal como la conocemos– se acabaría.
Pero eso no sucede –al menos por ahora– porque la Tierra recibe energía solar, una parte de la cual –fotosíntesis mediante– es transferida a las moléculas que componen los alimentos. Cuando comemos, incorporamos esa energía al organismo y así evitamos que las moléculas de nuestro cuerpo consigan el objetivo de dejar de moverse, lo que llevaría a la muerte.
En definitiva, el logro máximo al que puede aspirar cualquiera de estas partículas haraganas es el de alcanzar un estado en el cual su energía sea la mínima posible.
Las proteínas son moléculas y, por lo tanto, no escapan a esta regla. Por eso se pliegan, buscando lograr la conformación tridimensional que contenga la menor cantidad posible de conflictos energéticos, es decir, aquella en la cual la molécula esté menos “tensionada”. Por ejemplo, vimos que el agua tensiona las zonas hidrofóbicas de la proteína y, entonces, la molécula se pliega para tratar de reducir esas tensiones que la agobian.
Pero esto solo explica por qué las proteínas se pliegan y no cómo llevan a cabo las innumerables funciones que sostienen la vida. Dicho de otro modo, la propiedad de plegarse no es lo único que hace que una proteína funcione.
Eternas insatisfechas
Se dice que las proteínas “respiran”. Los propios científicos utilizan ese verbo para describir el movimiento oscilatorio que efectúan estas moléculas cuando realizan alguna función. Por ejemplo, la ferritina es una proteína presente en nuestro organismo que tiene la forma de un casquete hueco dentro del cual almacena hierro para que esté disponible cuando lo necesitemos. Cuando la ferritina “guarda” a este mineral en su interior, tiene una conformación tridimensional determinada y cuando “lo suelta” adopta una conformación alternativa. Lo mismo sucede con la hemoglobina –cuando toma y cede oxígeno– y con muchas otras proteínas.
Ese movimiento “de ida y vuelta” entre dos o más conformaciones –que es lo que permite que una estructura proteica realice una determinada acción– es provocado por un estado de insatisfacción permanente que padecen estas proteínas, que se debe a que no consiguen alcanzar el ansiado momento de mínima energía.
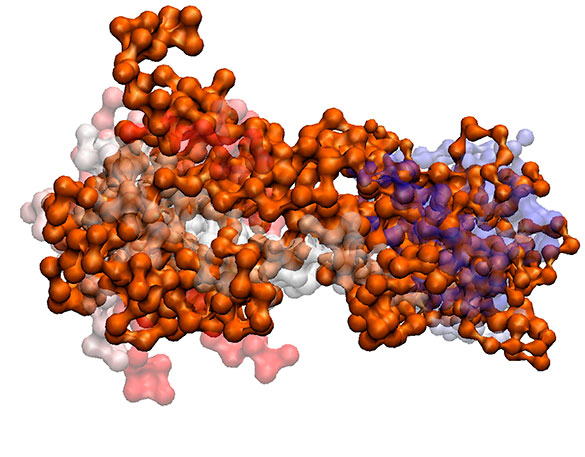
Es decir, el plegado no es suficiente para lograr la deseada tranquilidad. Y esto es así porque las proteínas establecen relaciones con numerosos componentes celulares –son las moléculas de interacción por excelencia– y en esa vinculación se producen conflictos energéticos que las desestabilizan. En este contexto, la proteína “prueba” diferentes configuraciones tridimensionales tratando de alcanzar el estado de mínima energía. Pero no lo logra. A este fenómeno se lo denomina “frustración”. Un término usado originalmente por la Física para referirse a aquellos sistemas que no consiguen un estado de mínima energía en todas sus interacciones.
Así, las proteínas nunca pueden estar completamente satisfechas. Pueden contener algunas regiones con interacciones favorables, es decir, cuyo contacto con otra molécula reduce la frustración, y zonas que al interactuar con otras partículas tienen un conflicto energético –se “tensionan”– y pueden llegar a estar altamente frustradas. Una elevada frustración puede atentar contra la estabilidad de la molécula.
Frustratómetro
La frustración es un concepto útil para comprender el comportamiento biológico de las proteínas. Mediante el análisis de cómo se distribuye la energía en la molécula y la determinación de las regiones donde la frustración es alta, pueden identificarse los lugares más inestables de estas macromoléculas, que generalmente coinciden con los denominados “sitios activos”, es decir, las zonas de la proteína responsables de llevar a cabo una determinada acción.
Pero medir la distribución de la energía en estas moléculas no es tarea fácil, porque las fuerzas que actúan sobre ella son débiles y efímeras. No obstante, un grupo de investigadores de la Facultad de Ciencias Exactas y Naturales de la UBA (Exactas-UBA) diseñó un programa de computación que permite calcular la energía total del sistema en pocos minutos.
“Es un algoritmo muy sencillo. Tanto es así que los cálculos se podrían hacer también manualmente, pero tardaríamos unos tres años para cada proteína”, comenta el doctor Diego Ferreiro, investigador del CONICET en el Laboratorio de Fisiología de Proteínas, quien es uno de los autores del programa, que está disponible para ser utilizado libremente.
Lo bautizaron “frustratómetro”. “Empezó como un chiste y después le quedó ese nombre”, sonríe.
El programa informático posibilita, para una determinada proteína, calcular la energía total del sistema. Después, vuelve a hacer ese cálculo cambiando uno de sus aminoácidos por otro. Luego repite la cuenta mutando otro distinto y así sucesivamente hasta, si se desea, probar todas las combinaciones posibles. Finalmente, el algoritmo compara la energía total de cada uno de esos “mutantes” que se produjeron.
“Esto permite comprobar que hay lugares de la molécula en donde el cambio de un aminoácido por otro no influye demasiado en la cantidad de energía y que hay otros lugares en donde la mutación influye mucho. Allí donde influye mucho, lo que el programa también te dice es si ese cambio es o no favorable en términos energéticos”, explica Ferreiro.
En general, los resultados muestran que, en promedio, un 50% de los aminoácidos de una proteína pueden ser cambiados sin provocar efectos significativos en su conformación tridimensional, mientras que alrededor de un 40% de los aminoácidos obedecen al principio de mínima frustración, o sea, favorecen la conformación de la proteína. En definitiva, solo un pequeño porcentaje de los aminoácidos son desfavorables, es decir, forman parte de regiones altamente frustradas.
“La distribución en el espacio de esos sitios altamente frustrados no es al azar, sino que están agrupados conformando parches que suelen corresponderse con un sitio funcional, un sitio activo, de la proteína”, señala Ferreiro, y mientras ceba un amargo, ilustra con un ejemplo: “Supongamos que este mate es una proteína. El sitio funcional sería el agujero para poner la yerba y la bombilla. El resto de la estructura tiene que ver con la función pero no de manera específica. También, lo que vemos es que la superficie del agujero está toda en una región, no está distribuida por todo el mate. De la misma manera, los aminoácidos que están en los sitios altamente frustrados, que conforman el sitio funcional de la proteína, se encuentran agrupados en una misma región del espacio, que generalmente está ubicada en la superficie de la molécula”.
Ferreiro cuenta que, en algunos casos, el análisis de proteínas con el frustratómetro reveló la presencia de parches de aminoácidos conformando regiones con alta frustración energética en lugares de la molécula que no se corresponden con el sitio funcional. “Tal vez son sitios activos que cumplen funciones que todavía no conocemos”, especula.
Motor vital
“Las proteínas tienen que ser necesariamente estables como para poder plegarse y suficientemente inestables como para poder funcionar”, dispara Ferreiro, resumiendo en una oración el difícil equilibrio que sostienen estas macromoléculas ante los conflictos energéticos que soportan permanentemente.
Se trata de un equilibrio meta-estable (así se lo llama) que es, precisamente, lo que les otorga su particular versatilidad.
Las proteínas respiran, se frustran, tienen conflictos… sin embargo no están vivas. Al menos, de acuerdo con el criterio “oficial” de vida. Porque existe un tipo de proteínas, los “priones”, cuyo comportamiento podría asemejarse al de un ser vivo.
En cualquier caso, lo que sí podría decirse es que la frustración es el motor que “le da vida” a las proteínas.